DPARSF预处理报错
各位老师,晚上好。
我在用DPARSFA作数据预处理的时候报错如下,然后换了DPARSF还是一样的报错。但是单独用SPM8做头动校正又可以,实在不知道是哪里出了问题。
希望老师们不吝赐教,谢谢!

然后这是我的设定
- Read more about DPARSF预处理报错
- 1 comment
- Log in or register to post comments
- 7272 reads
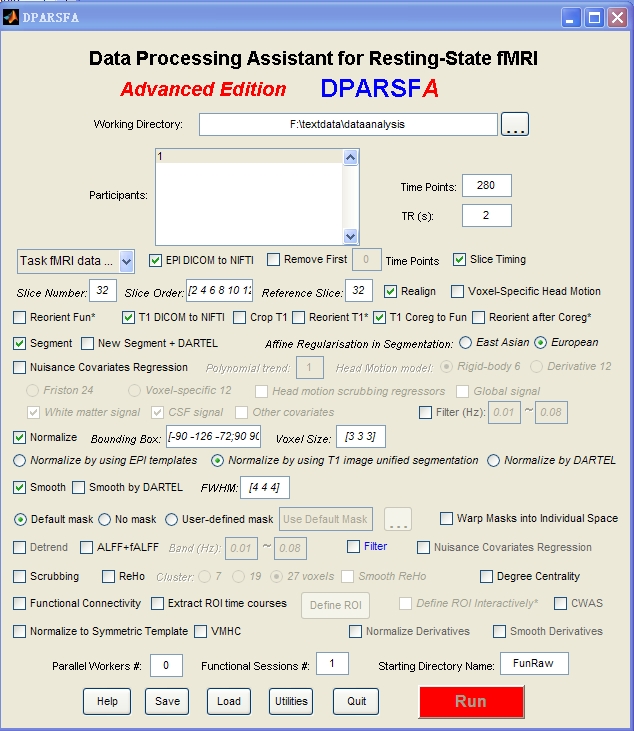
各位老师,晚上好。
我在用DPARSFA作数据预处理的时候报错如下,然后换了DPARSF还是一样的报错。但是单独用SPM8做头动校正又可以,实在不知道是哪里出了问题。
希望老师们不吝赐教,谢谢!

然后这是我的设定

 Converting T1 Images:Sub_001 OK
Converting T1 Images:Sub_001 OK
各位老师好:
我想用您开发的REST-GCA做任务态的GCA分析,可是看您的文献中提到rest-gca只适用于连续的任务态数据。我的数据不是连续任务态,是一很简单的组块设计的静息与任务等时相间的,并且我能很明确的把任务态的时间点全部提取出来,重新组成类似连续的任务态数据!不知道这样可不可以用rest-gca分析处理?此方法可行不可行?
望老师有时间给予解答与指导!谢谢!
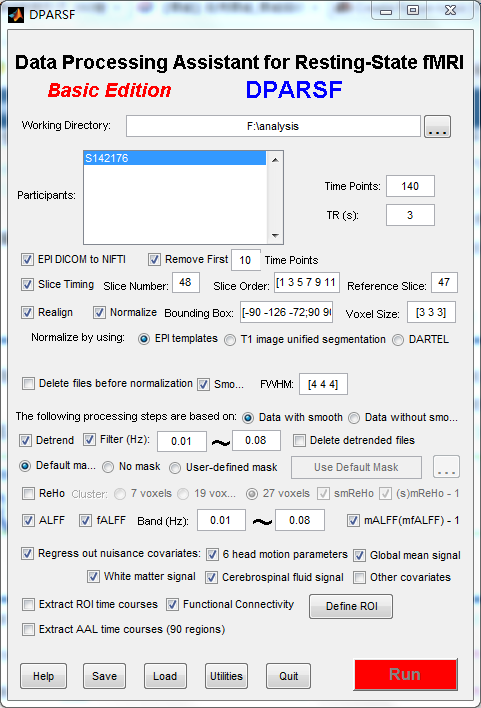
下了DPABI用dparsf基本版出错,整个DPABI文件夹是add with subfolds添加进去的,matlab2013a,REST1.8,一点击Run就出错
Undefined function 'DPARSF_run' for input arguments of type 'struct'.
老师,我现在在用DPARSF做图像的处理。看您的视频中所做的有关功能连接的都是静息态的。
我们现在设计的是在一个视觉刺激下检测fMRI的BOLD像。请问在有事件刺激的条件下能做功能连接吗?需要额外测量静息态的图像作为参考吗?
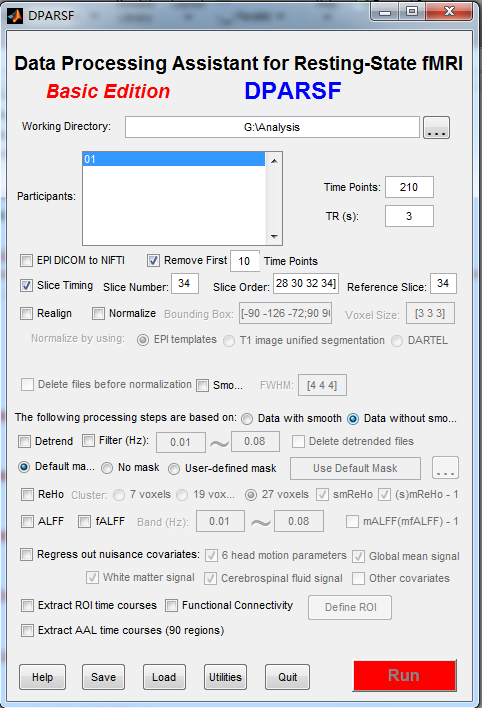
错误报告如下:
------------------------------------------------------------------------
老師, 我這次run DPABI出現了以下錯誤
以往run DPARSFA都不會有的
是程式更新的關係, 還是哪個步驟出錯了呢
謝謝老師
Moving Coviables Removed Files:NL1507 OK
??? Index exceeds matrix dimensions.
Error in ==> DPARSFA_run>(parfor body) at 2672
MatFilename=[AutoDataProcessParameter.DataProcessDir,filesep,'T1ImgSegment',filesep,AutoDataProcessParameter.SubjectID{i},filesep,MatFileDir(1).name];
FOV:RL(mm) 220
AP(mm) 220
FH(mm) 176
Voxel size
RL(mm) 3.44
AP(mm) 5
Slice thickness(mm) 5
Recon voxel size(mm) 1.53
Fold-over suppression no
Reconstruction matrix 144
SENSE yes
P reduction(AP) 1.8
Pos factor 1
Slices 32
Slice gap(mm) 0.5
Slice orientation transverse
fold-over direction AP
fat shift direction P
主讲:万小红
主持人:臧玉峰
时间: 上午10:00
日期:2014年9月29日(周一)
地点:杭州师范大学恕园4号楼206
Abstract: